DNA no oceano se degrada de forma mais complexa do que modelos tradicionais indicam e pode alterar leitura da biodiversidade marinha
destaque-4Estudo indica que modelos tradicionais podem distorcer estimativas sobre presença de espécies no oceano
A forma como o DNA ambiental (eDNA) se degrada no oceano é mais complexa do que os modelos tradicionalmente utilizados na ciência sugerem, o que pode influenciar diretamente a interpretação de dados sobre a presença e a distribuição de espécies marinhas. A conclusão é de um estudo internacional que combinou revisão de literatura, experimentos controlados e modelagem de transporte oceânico para analisar o comportamento do material genético após sua liberação no ambiente.
O trabalho, intitulado “Beyond Exponential Decay: How Biphasic and Delayed Decay Dynamics Shape Marine eDNA Dispersal”, é assinado por Mohamed Yosri Zanni, Verena M. Trenkel, Camille Albouy, Ana C. Vaz, pesquisadora do Instituto Nacional de Pesquisas Oceânicas (INPO), Claire B. Paris e Robin Faillettaz, e foi publicado em 2026 na revista Ecology and Evolution.
Modelos simplificados podem não representar o processo real
O eDNA é o material genético liberado por organismos no ambiente, como células, fragmentos de tecido ou excreções, e tem sido amplamente utilizado para monitoramento não invasivo da biodiversidade em ambientes aquáticos. A partir da análise desse material, é possível detectar espécies e inferir padrões ecológicos sem a necessidade de captura direta dos organismos.
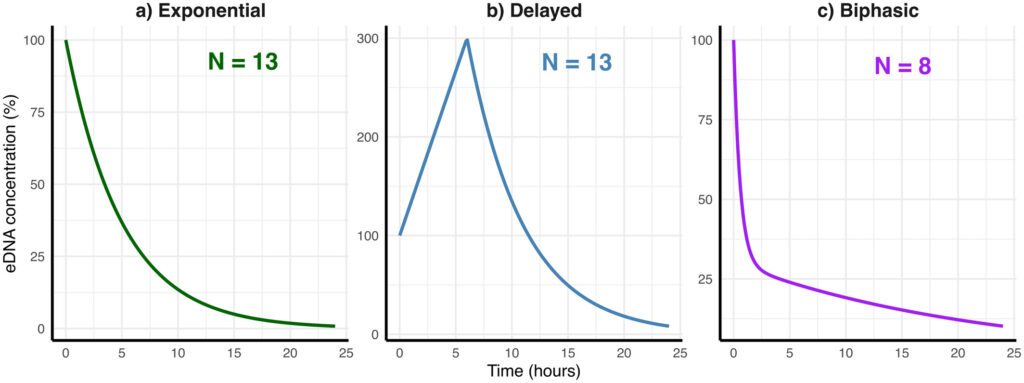
Até agora, muitos estudos assumem que o eDNA se degrada segundo um padrão exponencial simples, no qual sua concentração diminui continuamente ao longo do tempo. No entanto, o novo trabalho mostra que esse modelo nem sempre descreve adequadamente o comportamento observado no ambiente marinho.
O estudo combinou três abordagens complementares: uma revisão de experimentos publicados sobre degradação de eDNA, um experimento em laboratório com variação de temperatura e a aplicação de modelos de transporte oceânico baseados em rastreamento de partículas.
Os autores identificaram que a degradação do eDNA pode seguir dinâmicas mais complexas, incluindo padrões bifásicos – com uma fase inicial de rápida redução seguida por uma fase mais lenta – e padrões retardados, nos quais a concentração de DNA pode inicialmente se manter estável ou até apresentar aumento no número de cópias de eDNA antes do início do declínio.
Os resultados mostram que esses padrões não exponenciais foram observados na maioria dos estudos analisados e também nos experimentos conduzidos pelos autores, especialmente nas primeiras horas após a liberação do material genético no ambiente.
Evidências experimentais e modelagem oceânica
As simulações indicam que a escolha do modelo de degradação influencia diretamente as estimativas de dispersão do eDNA no oceano. Em comparação com o modelo exponencial simples, dinâmicas alternativas podem resultar em concentrações significativamente diferentes ao longo do tempo e do espaço, chegando a valores até quatro vezes maiores após 24 horas, dependendo do padrão de decaimento considerado.
De acordo com o estudo, assumir um modelo simplificado pode levar a interpretações imprecisas sobre a presença ou ausência de espécies, especialmente em ambientes marinhos, onde processos físicos, químicos e biológicos atuam simultaneamente sobre o transporte e a degradação do eDNA.
Os autores destacam que o uso exclusivo de um modelo exponencial pode resultar em subestimação ou superestimação da quantidade de DNA liberado pelos organismos, dependendo das condições ambientais locais.
A principal contribuição do estudo é demonstrar que a escolha do modelo de degradação do eDNA não é apenas um detalhe metodológico, mas um fator determinante para a interpretação dos dados. Ao incorporar dinâmicas mais realistas, como os padrões bifásicos e retardados, os modelos de transporte de eDNA tendem a representar de forma mais fiel os processos que ocorrem no ambiente marinho.
Os autores concluem que considerar diferentes tipos de degradação é essencial para aprimorar a confiabilidade dos estudos baseados em eDNA e para avançar no uso dessa ferramenta no monitoramento da biodiversidade marinha.
